GRO-seq:新生RNA測序服務
項目簡介
GRO-seq (Global nuclear Run-On sequencing) 是一種專門測量新生 RNA 的方法[1],可用於係統鑒定 eRNA 分子。該方法通過對細胞進行迅速冷凍,使細胞核內正在轉錄的複合體處於凍結狀態,然後提取細胞核,加入 Run on 緩衝液,使其重新恢複 RNA 的轉錄。利用抗 BrdU 抗體提取帶 BrU 標記的新生成 RNA ,用於下一步高通量測序分析。新生 RNA 的變化直接反映了轉錄調控的多種機理,通過 GRO-seq 技術,可以觀測到基因組水平正在進行的轉錄,繪製所有參與 RNA 聚合酶位置、數量和定向的高分辨率圖譜。

實驗流程
測序方案
Illumina NextSeq 6000
測序平台
SE 75
測序模式
40 M
數據量
送樣要求
1.具備條件的,可以把細胞核分離好液氮速凍並幹冰運輸。
2. 不bu具ju備bei前qian期qi準zhun備bei條tiao件jian的de,需xu提ti供gong活huo細xi胞bao及ji配pei套tao培pei養yang基ji,常chang溫wen運yun輸shu。如ru需xu進jin行xing細xi胞bao前qian處chu理li,請qing提ti供gong詳xiang細xi說shuo明ming和he相xiang關guan材cai料liao,並bing收shou取qu相xiang應ying處chu理li費fei用yong。
1x10⁷個
細胞數量
人,大小鼠
僅限物種
應用與分析
應用範圍
1、取代常規RNA-seq,精準檢測實時轉錄狀態的基因表達
2、精確定位基因的轉錄位置和轉錄方向
3、發現直接作用的靶標基因
4、發現新的轉錄本,包括非編碼RNA
5、鑒定eRNAs分子
生物信息分析
1. 數據產出統計,對原始測序數據去接頭、去低質量 reads、去汙染;
2. 測序序列與參考基因組序列的比對,Reads在全轉錄組的分布;
3. Reads在轉錄起始位點(TSS)附近的meta分析;
4. 轉錄暫停基因分析
5. eRNA分析
6. 差異基因分析
7. 差異基因 GO 功能聚類分析及KEGG生物通路富集分析
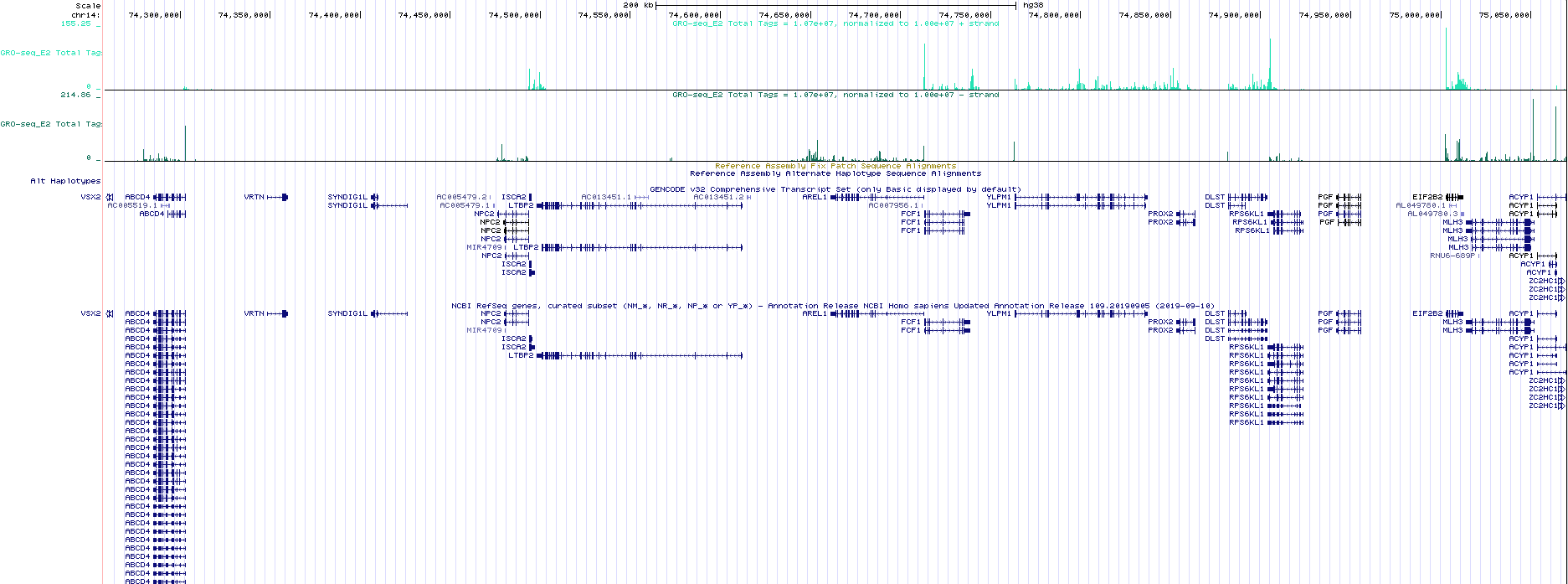
圖1. gro-seq數據在UCSC基因組瀏覽器中可視化bed文件
表觀生物實測數據
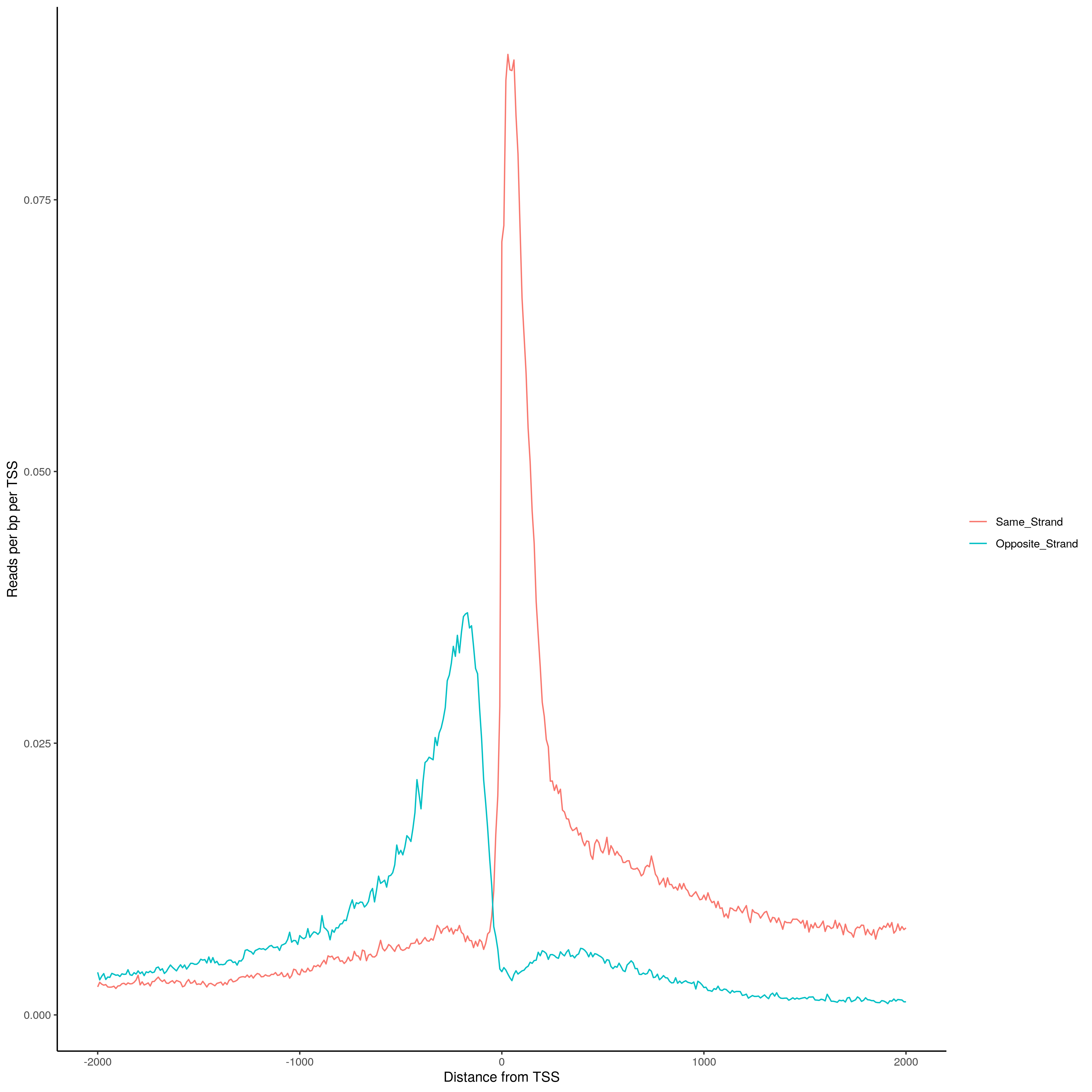
圖2. TSS距離直方圖
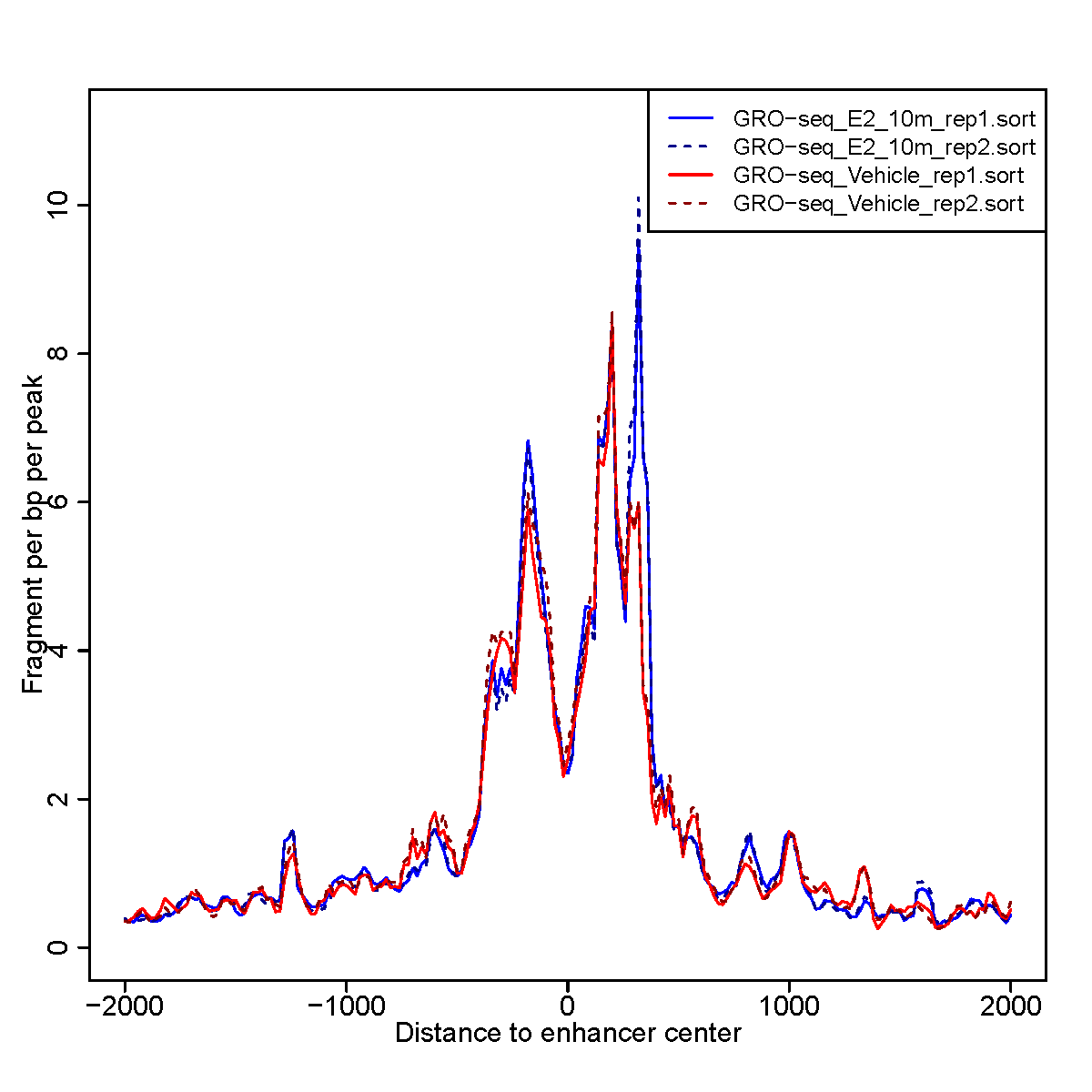
圖3. 所有樣品均位於增強子中心附近的gro-Seq信號

圖4. 兩種條件下暫停索引變化箱形圖

圖5. TSS周圍活躍基因的條件依賴性轉錄變化的熱圖
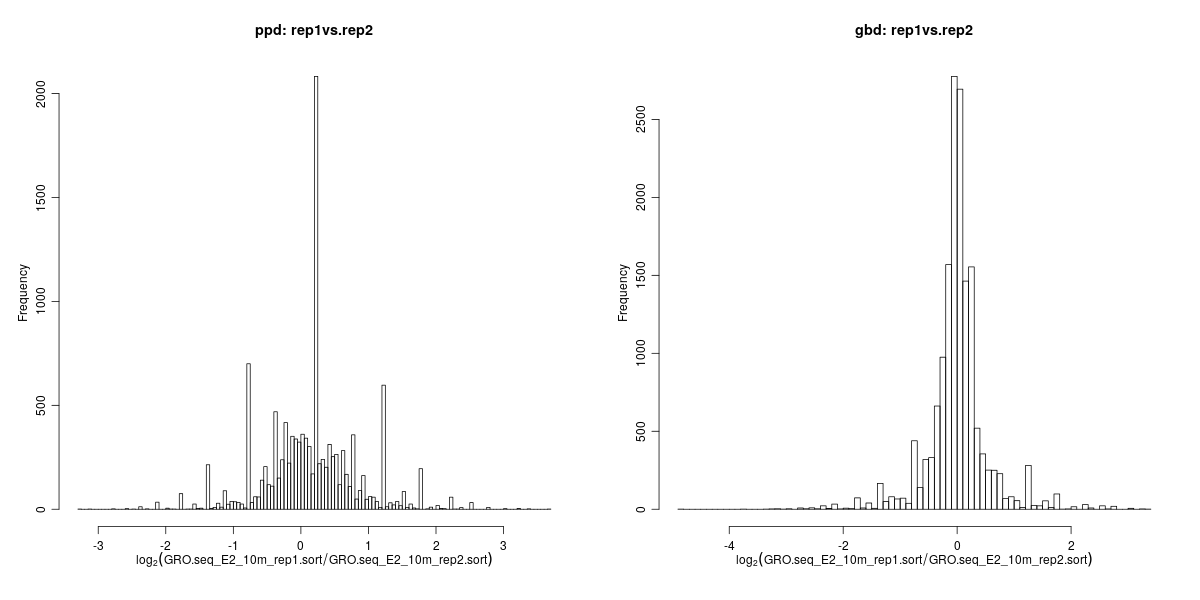
圖6. 條件1下重複樣本之間轉錄變化的直方圖
參考文獻
Core L J, Waterfall J J, Lis J T. Nascent RNA sequencing reveals widespread pausing and divergent initiation at human promoters[J]. Science, 2008, 322(5909): 1845-1848.
Danko C G, Hyland S L, Core L J, et al. Identification of active transcriptional regulatory elements from GRO-seq data[J]. Nature methods, 2015, 12(5): 433-438.
